
Automatische Übersetzung anzeigen
Dies ist eine automatisch generierte Übersetzung. Wenn Sie auf den englischen Originaltext zugreifen möchten, klicken Sie hier
#Neues aus der Industrie
{{{sourceTextContent.title}}}
Vollautomatische Bibliotheksvorbereitung bildet eine neue Matrix für die begleitende Diagnostik von Tumoren
{{{sourceTextContent.subTitle}}}
Vollautomatische Bibliotheksvorbereitung bildet eine neue Matrix für die begleitende Diagnostik von Tumoren
{{{sourceTextContent.description}}}
Der erste Konsens über die "Automatisierung und Standardisierung der Next-Generation-Sequenzierung in der klinischen Praxis", der von der Abteilung für Medizinische Labortechnik der Chinesischen Gesellschaft für Biomedizinische Technik geleitet wurde, wurde Ende 2023 im "Chinese Journal of Biomedical Engineering" veröffentlicht. Mit der Entwicklung der Tumor-Begleitdiagnostik und der Verbesserung der Automatisierung der Bibliotheksvorbereitung hat Feishuo Biotech als molekulardiagnostisches Unternehmen, das F&E, Produktion und Vertrieb von In-vitro-Diagnosereagenzien integriert, eine Reihe von molekularen Nachweisprodukten für die Tumordiagnose, Typisierung, Überwachung und das Screening auf der Grundlage der NGS-Technologieplattform entwickelt. Feishuo Biotech folgt aktiv dem Konsens und hat eine spezielle automatisierte Lösung für die NGS-Bibliotheksvorbereitung auf den Markt gebracht, die die Automatisierung und Standardisierung von Prozessen wie der Nukleinsäureprobenvorbereitung, der Bibliotheksvorbereitung und der Bibliotheksqualitätskontrolle effizient umsetzt und so die Anwendungskette für Gentests weiter verbessert und die Gesamtstärke und Wettbewerbsfähigkeit der Gesamtlösung für den Benutzer erhöht.
Qualifikationen und Patenttechnologien
Das Unternehmen verfügt über ein starkes Forschungs- und Technologieteam, das mit Hochdurchsatz-Sequenzierungsplattformen, digitalen PCR-Plattformen, fluoreszierenden quantitativen PCR-Plattformen, Nukleinsäure-Massenspektrometrie-Plattformen usw. ausgestattet ist. Auf dieser Grundlage hat es unabhängig mehr als 40 Produkte entwickelt, 41 inländische Patente und 3 internationale PCT-Patente angemeldet sowie 7 Erfindungspatente, 2 Gebrauchsmuster und 12 Software-Urheberrechte erhalten.
Produkt Reagenzienkit
Das Unternehmen verfügt über fortschrittliche Einrichtungen und GMP-Workshops nach internationalem Standard sowie ein solides Qualitätsmanagementsystem, das durch das süddeutsche Qualitätsmanagementsystem für Medizinprodukte nach TÜV ISO13485 zertifiziert ist. Gegenwärtig haben mehrere Reagenzienkits die CE-IVD-Zertifizierung und die NMPA-Zertifizierung erhalten, weitere befinden sich im Zertifizierungsverfahren.
Zulassungsbescheinigung für Medizinprodukte der Klasse I, Reagenzienkit für Gensequenzierungsbibliotheken
Internationale EU-CE-IVD-Zertifizierung
Reagenzienkit zum Nachweis von Multigen-Mutationen in menschlichen Tumoren (Halbleiter-Sequenzierverfahren), Reagenzienkit zum Nachweis von BRCA1/2-Gen-Mutationen in Menschen (Hochdurchsatz-Sequenzierverfahren), Reagenzienkit zum Nachweis von mit der Strahlentherapie zusammenhängenden Genen (Hochdurchsatz-Sequenzierverfahren), Reagenzienkit zum Nachweis von Genom-SNPs in Menschen (Hochdurchsatz-Sequenzierverfahren), usw.
Registrierungszertifikat für Medizinprodukte der Klasse III
Kombiniertes NGS-Produkt zum Nachweis von Lungenkrebs-Multigenen "Reagenzienkit zum Nachweis von menschlichen EGFR/KRAS/BRAF/HER2/ALK/ROS1-Genmutationen (Halbleiter-Sequenzierungsmethode) (National Medical Products Administration Registration No. 20203400094)", Reagenzienkit zum Nachweis von menschlichen EGFR-Genmutationen (Multiplex-Fluoreszenz-PCR-Methode) (National Medical Products Administration Registration No. 20193400366), Reagenzienkit zum Nachweis von menschlichen K-ras-Genmutationen (Multiplex-Fluoreszenz-PCR-Methode) (National Medical Products Administration Registration No. 20223400275) usw.
Vollautomatische Maschine zur Vorbereitung und Auswertung von Bibliotheken
Um die Effizienz der begleitenden Diagnostik zu verbessern, verwendet unser Unternehmen das Reagenzienkit für den Nachweis von Genmutationen des humanen EGFR/KRAS/BRAF/HER2/ALK/ROS1-Gens (Halbleiter-Sequenzierungsmethode), das auf einer vollautomatischen NGS-Bibliotheksvorbereitungs- und -auswertungsmaschine basiert, und entwickelt eine erweiterte automatisierte Hochdurchsatz-Anwendung für begleitende diagnostische Tumortests. Um die Qualität und Effizienz des Testprozesses umfassend zu verbessern, wurde der Automatisierungsprozess dieser Plattform durch ein Moduldesign und ein verbessertes Tischlayout optimiert, um unterschiedlichen Durchsätzen bei der Bibliotheksvorbereitung gerecht zu werden und die Effizienz der Bibliotheksvorbereitung erheblich zu verbessern. Durch die Reduzierung der manuellen Arbeitsschritte um mehr als 90 % bei gleichzeitiger Sicherstellung einer qualitativ hochwertigen Bibliotheksvorbereitung werden die Hände des Laborpersonals entlastet, die Arbeitseffizienz verbessert und die Möglichkeit menschlicher Fehler effektiv reduziert und vermieden, wodurch präzise, zuverlässige, stabile und effiziente Ergebnisse gewährleistet werden.
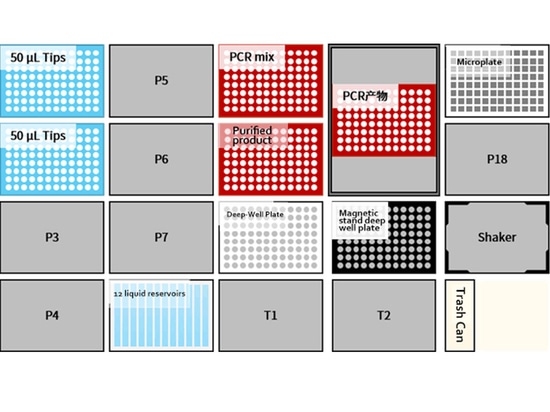
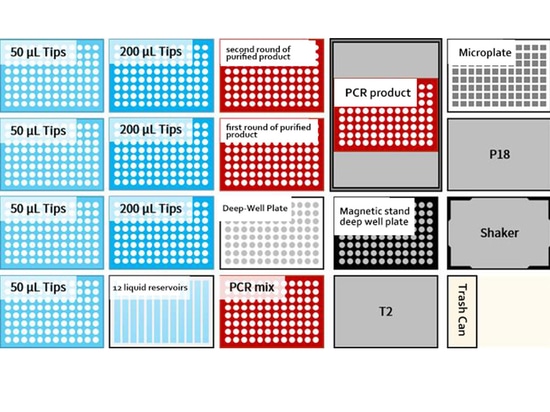
Layout der Arbeitsplatte
01 Niedriger Durchsatz: 8 Proben/Zeit
02 Mittlerer und hoher Durchsatz: 48 Proben/Zeit
Qualitätsanalyse
Die quantitative Analyse der Bibliothekskonzentration zeigt, dass die Einheitlichkeit der automatisierten Bibliotheksvorbereitung dem manuellen Betrieb überlegen ist. Die Peakkurve der Bibliotheksfragmentanalyse zeigt einen klaren Hauptpeak ohne Verunreinigungen. Die Ergebnisse der Kapillarelektrophorese zeigen, dass der Hauptpeakbereich der Bibliothek 200-300 bp beträgt.
In Zukunft wird unser Unternehmen die Anwendung und Entwicklung genetischer Testprodukte auf automatisierten Bibliotheksvorbereitungsplattformen weiter ausbauen, eine neue Matrix für die begleitende Tumordiagnostik schaffen, den Anwendungswert der Präzisionsdiagnose und -behandlung steigern und hochwertige Präzisionsdiagnoseleistungen für ein breites Spektrum von Tumorpatienten anbieten.


{{medias[59555].description}}
{{medias[59557].description}}
{{medias[59558].description}}

{{medias[59559].description}}




